Nat Genet:黄海亮/葛天合作开发跨人群精细映射(fine |
 |

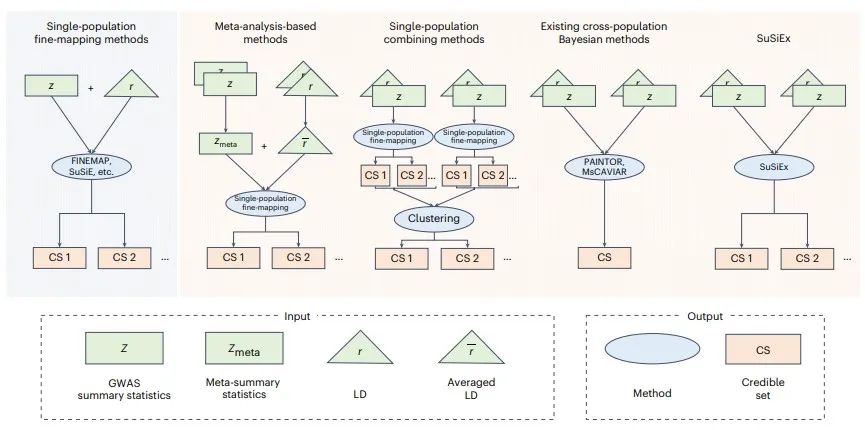
精细映射分析一览(Credit: Nature Genetics)
研究者首先进行了一系列全面的模拟,系统评估了SuSiEx的性能。通过改变群体间遗传相关性、因果突变数量、遗传力等模拟参数,从多个角度(如检测效力、覆盖度、准确度、分辨率、鲁棒性等)对SuSiEx进行了评估。模拟结果表明,SuSiEx在覆盖度、准确度和鲁棒性方面表现出色,并且相比单群体精细映射方法,SuSiEx具有更高的检测效力和分辨率。接下来,研究者将SuSiEx与其他现有方法(如单群体精细映射合并分析方法、基于元分析的精细映射方法、贝叶斯跨群体精细映射分析方法)进行比较,结果显示SuSiEx在易用性、分辨率和准确度等方面表现更佳。
随后,研究者将SuSiEx应用于不同人群生物样本库的数据分析。具体而言,他们将该方法应用于英国生物银行(UK Biobank)的欧洲人和非洲人群体数据,以及台湾生物银行(Taiwan Biobank)的东亚人群体数据。研究者筛选出25个在这两个数据库中共有的数量性状,并选出13,420个可能包含因果变异的基因组区域。通过使用SuSiEx分析三个人群的数据,研究人员共发现了14,361个99%置信集合(credible set),即该集合有99%概率包含因果突变。与仅使用单一人群数据的精细映射分析相比,SuSiEx在跨人群数据分析中发现了更多置信集合,其最佳位点的后验包含概率(Posterior Inclusion Probability, PIP)也更高,且后验包含概率大于95%的置信集合数量也显著增加。这些结果都凸显了SuSiEx方法及其在跨人群精细映射分析中的优越性。
最后,研究人员利用SuSiEx对精神分裂症进行了精细映射研究。他们使用了 精神类疾病基因组学研究联盟(Psychiatric Genomics Consortium, PGC) 提供的欧洲人和东亚人群体的精神分裂症GWAS汇总统计量和连锁不平衡信息【5】。SuSiEx在193个基因组关联区域中成功识别出215个99%置信度的置信集合,其中213个被推断为欧洲人群中的因果突变,95个被推断为东亚人群中的因果突变。在这213个置信集合中,有11个包含后验包含概率大于95%的突变位点。与预期一致,SuSiEx的表现优于已发布的PGC精细映射分析结果。
总体而言,文章介绍了一种精准高效的跨人群精细映射分析工具SuSiEx。通过整合多人群数据、明确建模群体特异性等位基因频率和连锁不平衡模式,SuSiEx发现了基因组中的更多因果变体,并可使用GWAS汇总统计量进行分析。
医药网新闻
- 相关报道
-
- 从“假基因”到“致病元凶”!Brain新研究:SSPOP基因复合杂合突变诱发儿童癫痫,多模型证实其功能与致病机制 (2025-10-15)
- Science:“吃不胖”的免疫学新解——T细胞胆固醇稳态是决定膳食脂肪吸收的关键 (2025-10-15)
- 迈威生物靶向 CDH17 ADC 创新药 7MW4911 临床试验申请获得 NMPA 批准 (2025-10-14)
- 西湖大学开发AI科学家,实现全自动科学发现,两周搞定人类科学家三年工作 (2025-10-14)
- Oncoscience:你的精子在“求救”?印度科学家发现,这些日常习惯正在偷走生育力! (2025-10-14)
- 腹痛便血反复?J Ethnopharmacol:“中医解法”被证实!芍药汤能精准激活肠干细胞,修复黏膜不反复 (2025-10-14)
- STTT:华西医院科学家发明可修复血脑屏障的纳米药物,可快速清除阿尔茨海默病毒蛋白、改善认知! (2025-10-14)
- Nature子刊:房颤竟是一种自身免疫疾病? (2025-10-14)
- Nature:为何男性和吸烟者更易患膀胱癌? (2025-10-13)
- AJRCCM:血液里的“预警信号”!科学家发现肺纤维化早期检测新希望 (2025-10-13)
- 视频新闻
-
- 图片新闻
-
医药网免责声明:
- 本公司对医药网上刊登之所有信息不声明或保证其内容之正确性或可靠性;您于此接受并承认信赖任何信息所生之风险应自行承担。本公司,有权但无此义务,改善或更正所刊登信息任何部分之错误或疏失。
- 凡本网注明"来源:XXX(非医药网)"的作品,均转载自其它媒体,转载目的在于传递更多信息,并不代表本网赞同其观点和对其真实性负责。本网转载其他媒体之稿件,意在为公众提供免费服务。如稿件版权单位或个人不想在本网发布,可与本网联系,本网视情况可立即将其撤除。联系QQ:896150040





















